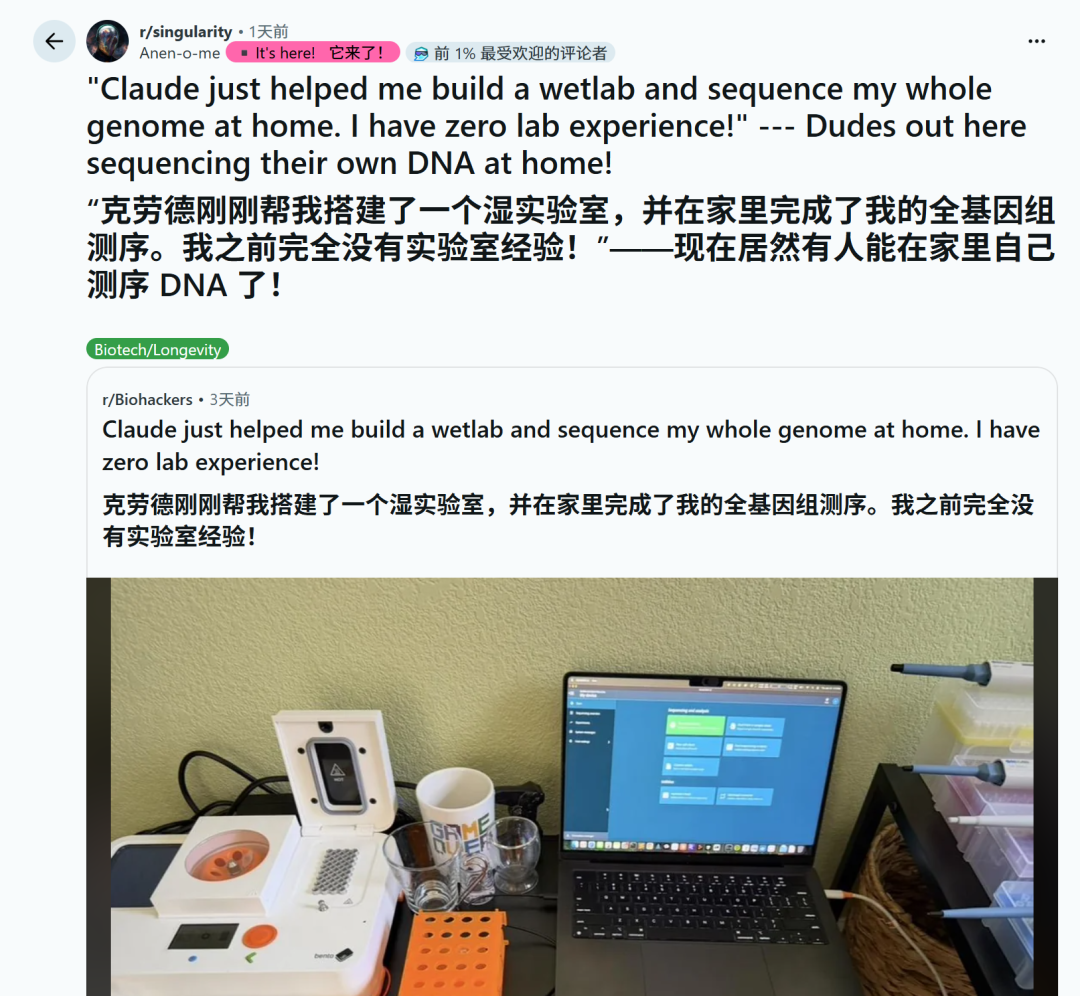
Aujourd’hui encore, Internet tout entier a été inondé de l’histoire de ce type post-00 ! Cet internaute nommé Seth Howes a utilisé un séquenceur portable et Claude pour réaliser indépendamment le séquençage complet du génome dans son salon et a réussi à retracer le mécanisme pathogène des maladies auto-immunes dans sa famille sur plusieurs générations.
Avec un séquenceur de la taille d'une clé USB et plusieurs modèles d'IA, Seth Howes, un jeune homme né dans les années 2000, a réalisé le séquençage du génome dans son salon et a résolu à lui seul le mystère de la maladie auto-immune de sa famille, resté entier pendant des décennies. En 2023, le coût de la réalisation d’une séquence complète du génome humain s’élèvera à 2,7 milliards de dollars, mais il n’a dépensé que 1 100 dollars !
Ces problèmes ont laissé d’innombrables cliniciens désemparés.
Aucun clinicien n’a été capable d’expliquer ces mécanismes auparavant. Après plus de dix ans de traitement et d’innombrables visites à l’hôpital, la réponse a finalement été trouvée dans mon propre salon.
Cette expérience est tellement choquante que le milieu de la biotechnologie est désormais sous le choc !
Le grand modèle de Claude a en fait transformé le séquençage génétique d'une activité à forte intensité de capital en un outil personnel.
Le lieu de recherche biologique n'est plus une machine coûteuse dans un laboratoire de pointe, ni une plate-forme publique dans une école de médecine, mais dans votre propre salon !

Laboratoire sur table, comprenant module chauffant, vortexeur, mini centrifugeuse, pipette, MinION
Maintenant, ce message a été publié sur Internet.
Les gens qui font des expériences en laboratoire depuis dix ans disent avec émotion : Vous êtes tellement professionnels.
Les personnes qui font de la recherche génétique affirment que ce projet de séquençage du génome correspond à leur champ de recherche.
Un patient souffrant de tumeurs a déclaré que cette expérience était d'une grande importance.

On peut dire qu’il s’agit d’une pratique DIY qui peut choquer toute la biosphère : dès lors, la recherche biologique brise le monopole des institutions et entre complètement dans l’ère des individus !
Il espère retrouver le pouvoir de décision de la vie après la douleur
Seth Howes est un ancien ingénieur d'Exolabs et est titulaire d'un doctorat en médecine d'Oxford et d'un doctorat en apprentissage automatique de l'Imperial College.
Les recherches de Seth ne sont pas nées d'un intérêt universitaire, mais d'une forte pression génétique familiale.
Sa famille souffre depuis longtemps de maladies auto-immunes à haut risque.
Alors qu'il menait des expériences, sa sœur, âgée de moins de 40 ans, a subi de graves lésions au foie dues à une maladie. Elle a dû attendre deux ans avant d’obtenir une source hépatique pour une intervention chirurgicale.

« Je ne me fais aucune illusion quant à la possibilité de guérir les maux de notre famille, mais je veux comprendre pourquoi notre corps continue de se ronger, génération après génération. »
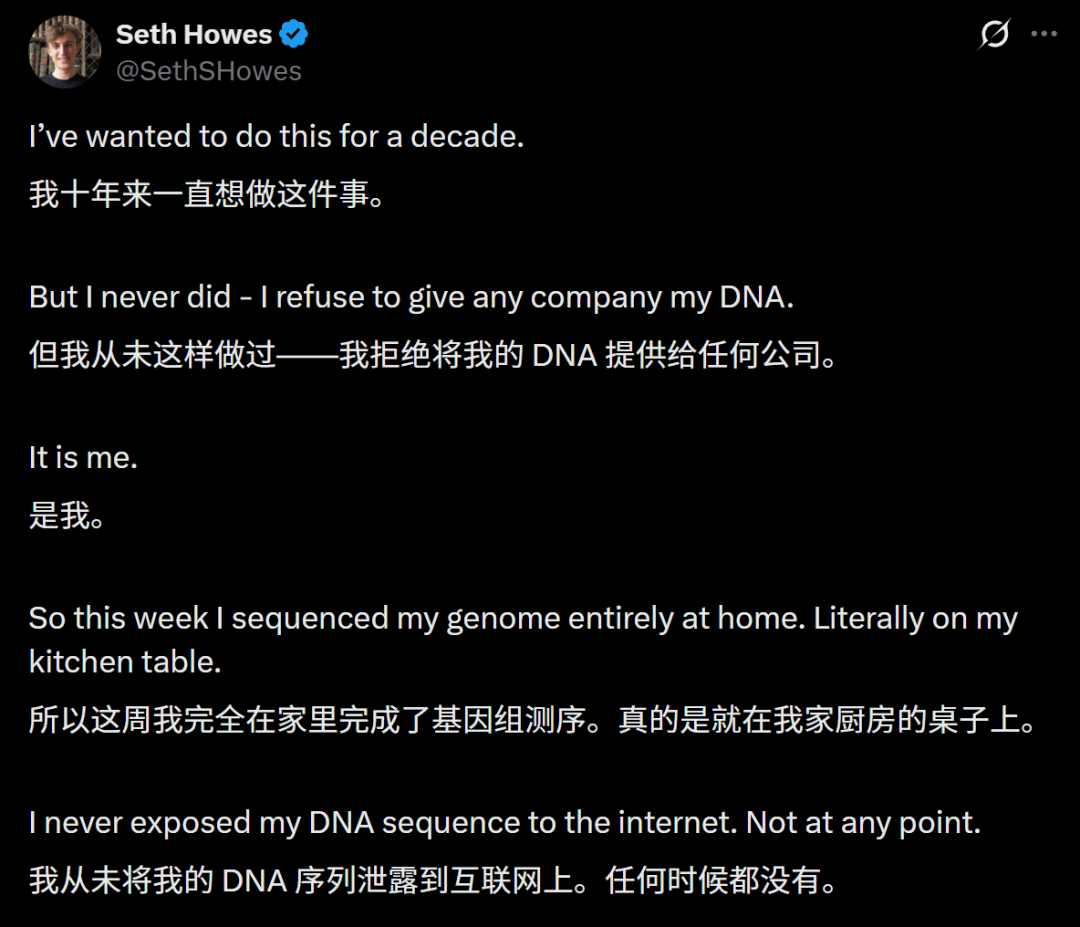
C'est cette curiosité pour le code sous-jacent de la vie, associée à la recherche de la confidentialité des données, qui l'a incité à décider de construire un établi « d'apothicaire numérique » dans son salon.
Après tout, selon lui, "vos données les plus privées ne devraient jamais quitter votre maison".
Technologie Core Black : bénédiction exponentielle de l’IA
Dans le passé, le séquençage du génome entier était l’apanage des grands laboratoires et coûtait des centaines de milliers de dollars.
La clé du succès de Seth réside cette fois dans la bénédiction de trois éléments.
Matériel : Un « lecteur de gènes » dans votre poche
Premièrement, en termes de matériel, il a utilisé le séquenceur Oxford Nanopore MinION.
Cet objet n’a que la taille d’une clé USB et peut lire des séquences d’ADN lorsqu’il est branché sur un ordinateur.

Il y a quelques années, la même chose aurait nécessité un séquenceur Illumina remplissant la pièce, une équipe dédiée et un budget à six chiffres.
Or, cet appareil, qui n’a que la taille d’une batterie externe, est rempli d’environ 2 000 nanopores (seulement 1 nanomètre de diamètre). Lorsque des fragments d’ADN traversent ces trous, les changements de microcourants provoqués seront enregistrés et convertis en codes génétiques.

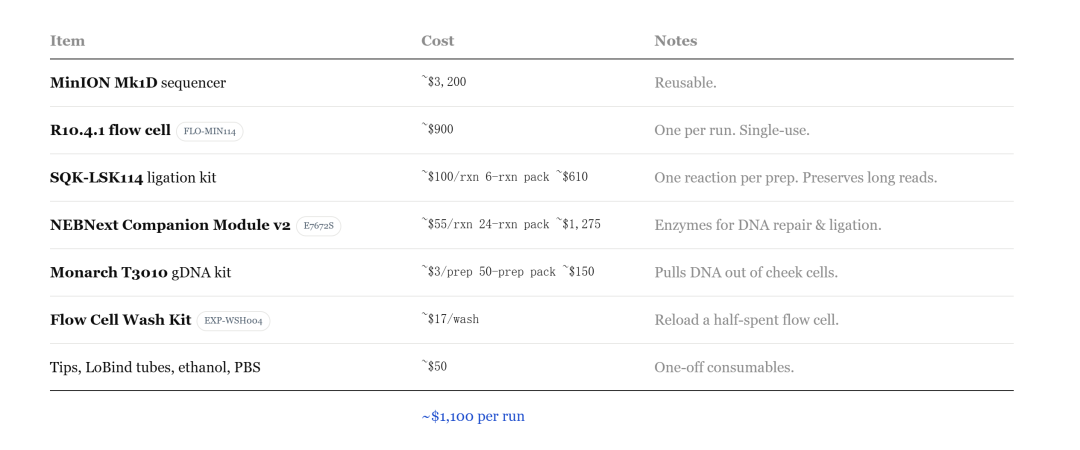
Cela réduit le coût du séquençage de plusieurs centaines de milliers de dollars à 1 000 dollars, et pourrait même chuter à 100 dollars à l'avenir.
On peut dire que MinION a transformé la « lecture de l'ADN » d'une activité à forte intensité de capital en une capacité basée sur des outils.
Tout comme les imprimantes 3D déplacent la « fabrication » de l’usine vers le bureau, MinION déplace le « séquençage » du laboratoire vers le salon.
Modèle IA : de la « lecture du code » à la « compréhension des fonctions »
Mais dans l’expérience, il ne suffit pas de lire les quatre bases A, T, C et G.
Trois milliards de paires de bases de données brutes se trouvent devant vous, et si vous ne savez pas ce qu'elles signifient, ce n'est qu'un tas de lettres.
C’est là que l’IA entre en jeu. Dans les expériences, deux modèles clés ont été utilisés.
Le premier est Evo2.
Il s'agit d'un modèle génomique de base développé par l'Institut Arc, avec une échelle de paramètres de 7 milliards et formé sur les données génomiques de plus de 120 000 espèces dans le monde. Ce qu'il peut faire, c'est : étant donné une séquence d'ADN, prédire la fonction biologique de cette séquence.
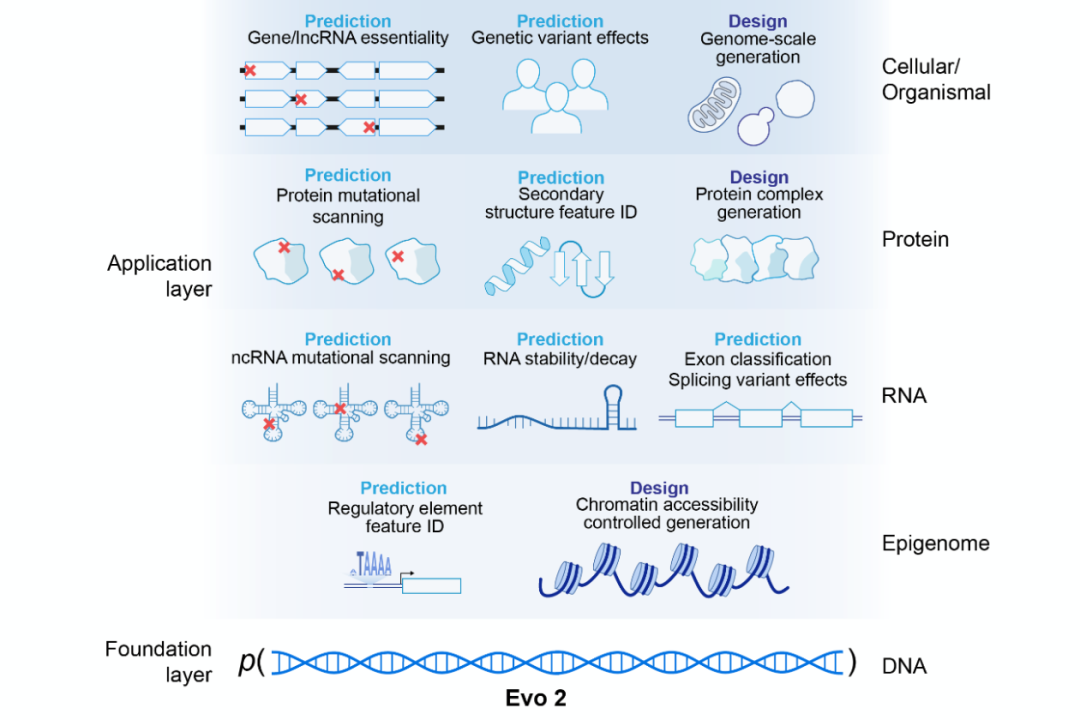
Vous devez l'avoir réalisé : il s'agit d'une version biologique de GPT !
GPT comprend le langage humain et Evo2 comprend le langage de la vie. La différence est que le livre lu par Evo2 contient 3 milliards de lettres.
Le deuxième est AlphaGenome.
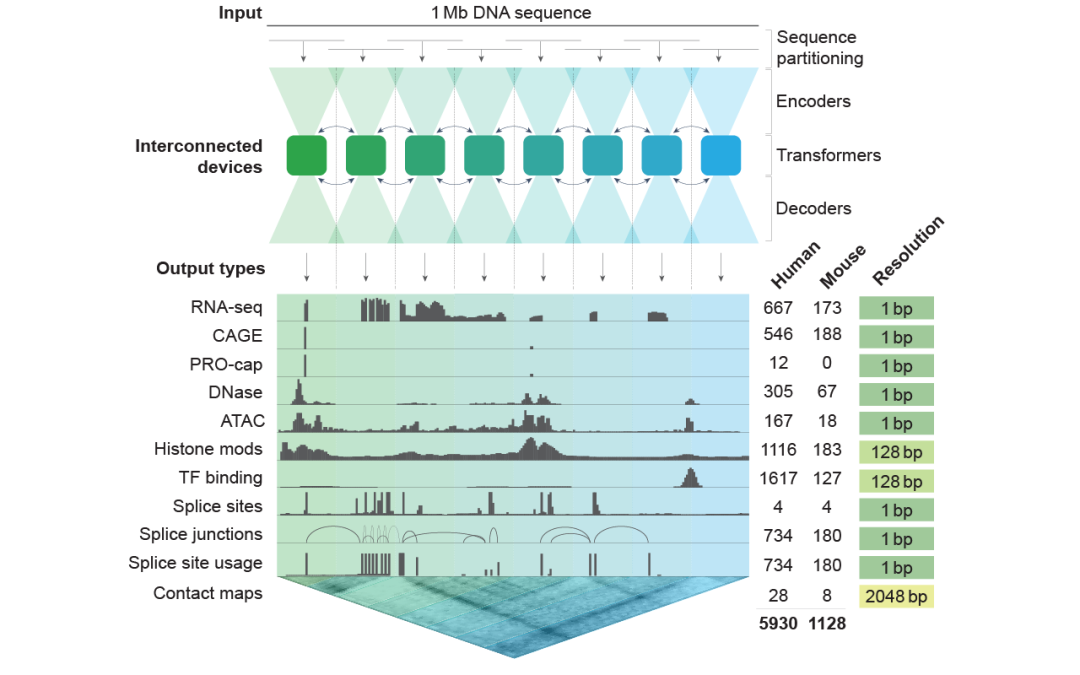
Produit par Google DeepMind, spécialisé dans la prédiction des fonctions du génome. Il vous indique non seulement « quelle protéine est codée par cet ADN », mais prédit également « quel impact une mutation sur ce site aura sur l'expression des gènes et la structure de la chromatine ».
De la « lecture de l'ADN » à la « compréhension du fonctionnement de l'ADN », ce saut prenait plusieurs mois à tout un laboratoire de biologie moléculaire pour le vérifier. Désormais, un modèle peut fonctionner pendant quelques heures seulement et les résultats seront disponibles.
Interface simplifiée : les grands modèles deviennent des « assistants de laboratoire »
En parlant de ça, le détail le plus surprenant dans toute cette affaire n’était pas le séquenceur ou le modèle du génome, mais Claude.
Seth a utilisé Claude pour générer le fichier BED pendant l'opération.
Les fichiers BED sont un format de données standard pour la génomique, enregistrant les informations de coordonnées de régions spécifiques du génome. Dans le passé, l'écriture de ce type de fichier nécessitait que des professionnels connaissant la bioinformatique l'écrivent manuellement ou utilisent des outils spécialisés en ligne de commande.
L'approche actuelle consiste à utiliser le langage naturel pour dire à Claude "générez un fichier BED pour que je couvre ces régions génétiques", et il sera généré.
Les opérations biologiques ont été reprises par les interfaces linguistiques.
L’ère des laboratoires personnels est arrivée
Or, la démocratisation du matériel (MinION), l’amélioration exponentielle de la compréhension de l’IA (Evo2 + AlphaGenome), et le lissage du seuil de fonctionnement par les interfaces linguistiques (Claude) constituent directement une chaîne complète de changement de paradigme.
Chaque lien seul n’est pas une nouvelle. Mais lorsque les trois anneaux se ferment en même temps, quelque chose ne va pas !
Un jeune homme curieux a résolu dans son salon un mystère qui échappait aux cliniciens depuis plus de dix ans.
L’impact de cet incident n’est pas que l’histoire personnelle de Seth soit légendaire, mais qu’elle révèle une courbe qui s’accélère.
La trajectoire descendante des coûts de séquençage est encore plus sévère que la loi de Moore.
En 2003, le coût de la séquence du génome humain s'élevait à 2,7 milliards de dollars. En 2007, ce chiffre est tombé à 10 millions. Il est tombé à 1 000 dollars en 2014. En 2024, certaines plateformes pourront déjà atteindre des prix inférieurs à 200 dollars.
Le prochain objectif est de 100 $.

La pente de cette courbe signifie que dans un avenir pas si lointain, le séquençage de votre propre génome pourrait coûter moins cher qu’un examen physique complet.
La première réaction de beaucoup de gens est : n’est-ce pas juste un projet de passe-temps pour geeks ? Qui parmi les gens ordinaires testerait son génome à la maison ?
Mais repensez, en 2010, combien de personnes pensaient que « les gens ordinaires utiliseraient des imprimantes 3D à la maison » ?
Chaque fois que la chaîne d’outils est fermée, la période de fenêtre entre les jouets de geek et les applications de masse est raccourcie. La période de fenêtre pourrait être plus courte cette fois-ci, car elle est motivée par une demande rigide.
Dossier d'expérience dans le salon : Comment « lire » son propre ADN à la maison ?
Les procédures opérationnelles complètes publiées par Seth montrent qu'en plus des pipettes de précision, bon nombre de ses équipements de laboratoire sont d'occasion sur eBay ou AliExpress.
Lors de la phase d’extraction de l’échantillon, il n’a pas effectué de prises de sang compliquées, mais a frotté l’intérieur de sa joue avec un tampon buccal stérile. Il a obtenu environ 5 à 7 microgrammes d’ADN avec un seul écouvillon, ce qui dépasse de loin le microgramme requis pour l’expérience.
L’échantillonnage adaptatif est l’atout de MinION.
Seth utilise un contrôle logiciel pour laisser le séquenceur effectuer un « criblage préliminaire » lors de la lecture des 500 premières bases de chaque fragment : s'il s'agit d'un gène lié au système immunitaire qui le préoccupe, continuez la lecture ; sinon, inversez la tension pour « cracher » le brin d'ADN et remplacez-le par le suivant.
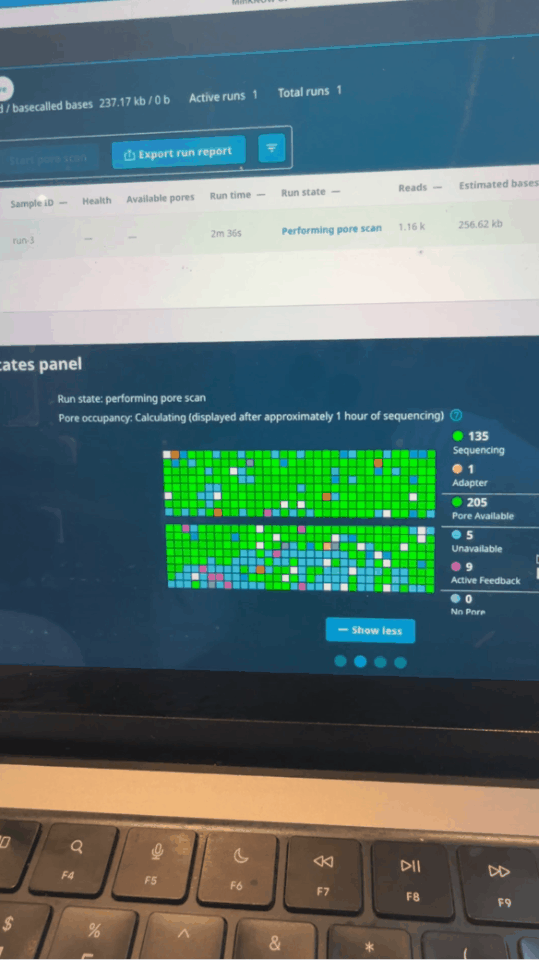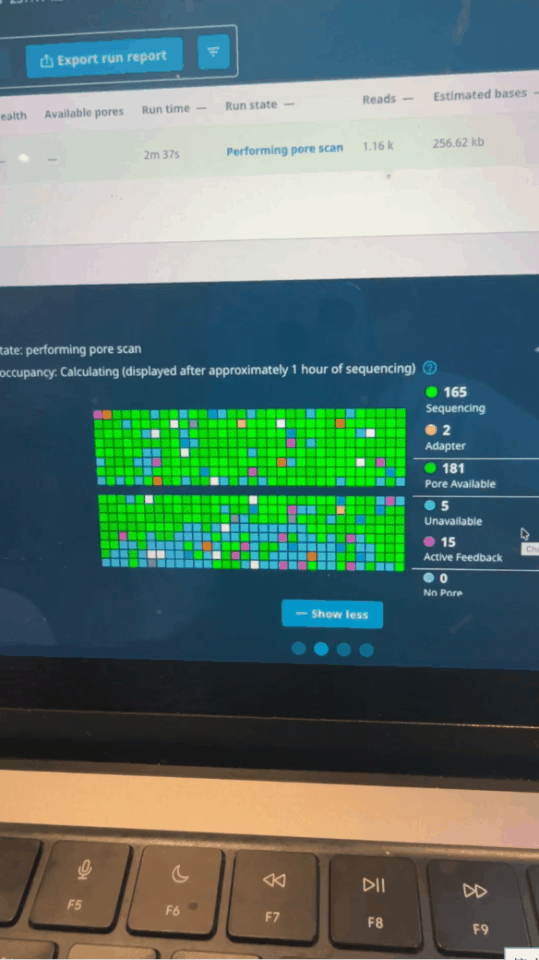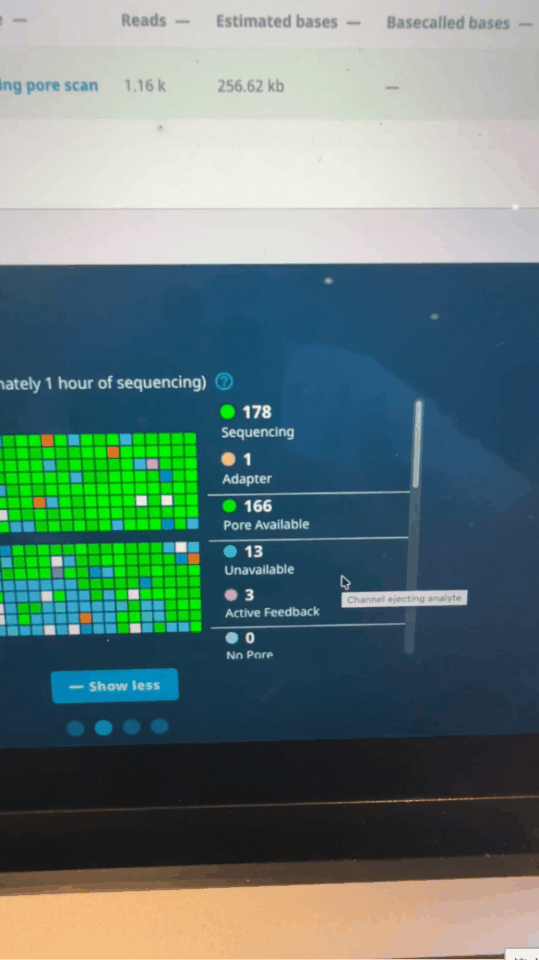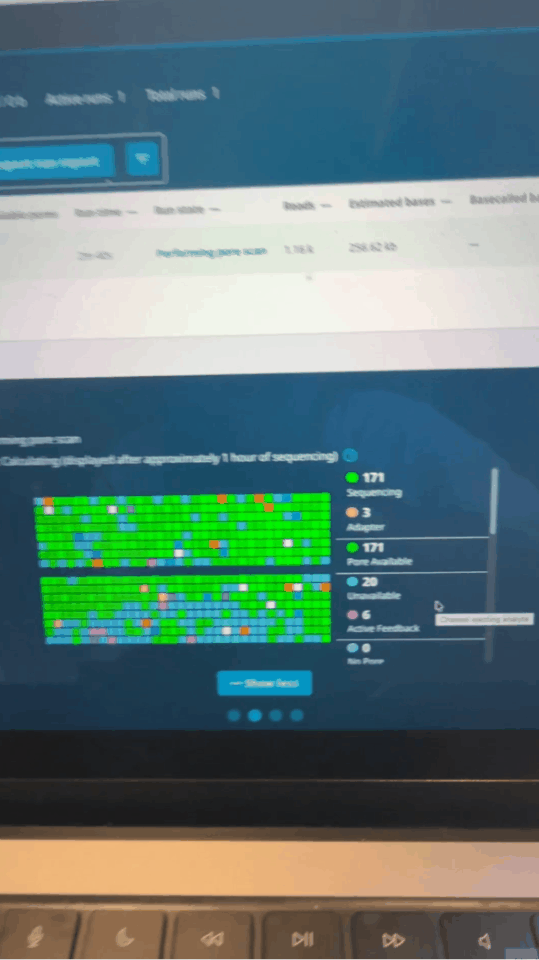
État d'activité des nanopores sur le panneau de commande MinKNOW quelques minutes après le début de l'analyse
Dans ce processus, il a utilisé Mac Studio de la puce M3 Ultra pour l'identification de base en temps réel, et a utilisé le DGX Spark de NVIDIA pour augmenter la vitesse d'analyse et garantir la puissance de calcul.
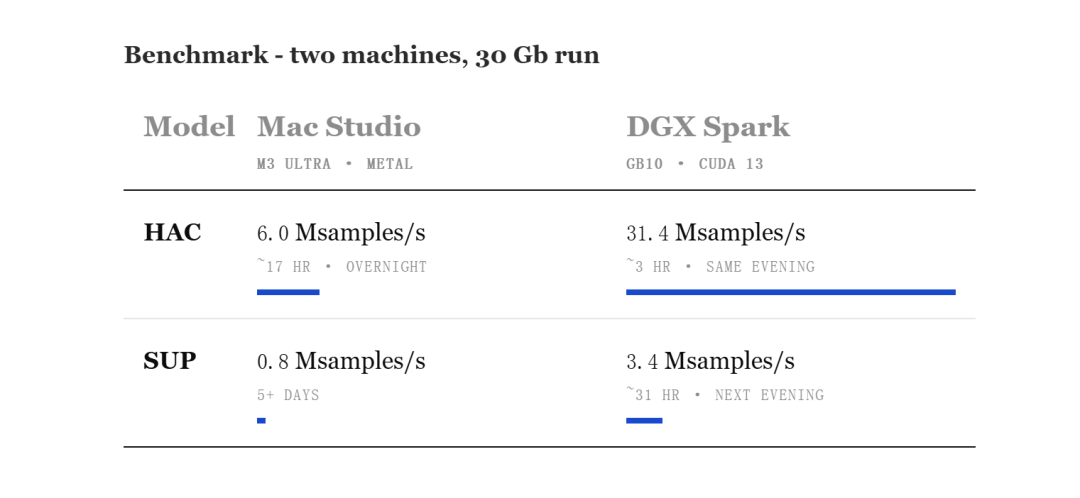

La biologie n'est plus un monopole individuel
Dans les années 1970, les ordinateurs étaient l’apanage des grandes organisations, puis les ordinateurs personnels sont arrivés, puis Internet.
La biologie suit le même chemin.
Le séquenceur est l'ordinateur personnel, le modèle de base du génome est le système d'exploitation et Claude est l'interface utilisateur. Lorsque les trois couches seront en place simultanément, le « moment PC » de la biologie arrivera.
L'après-midi où Seth a fini de séquencer son génome dans son salon a peut-être été la première image de ce moment.
Dix ans plus tard, 2026 sera probablement une année charnière.
L’importance de cette expérience va bien au-delà de la victoire d’un connaisseur de la technologie. Cela montre que la recherche biologique subit un changement de paradigme, passant du monopole institutionnel au mode du bricolage individuel.
Lorsque des opérations biologiques complexes seront simplifiées en conversations linguistiques par l’IA et lorsque des instruments coûteux deviendront abordables pour tous, les gens ordinaires seront en mesure d’analyser activement la logique sous-jacente de la vie.
Comme Seth l'a dit, il a découvert le plaisir de jouer avec des ordinateurs lorsqu'il était enfant en jouant avec des circuits génétiques. Cet « esprit geek » ouvre une nouvelle ère.
Combien de miracles l’IA va-t-elle créer ensuite ?